近日,我院袁玉峰博士在分析化学领域顶级期刊《Analytical Chemistry》发表题为“Precisely Identifying Growth Phases of Living Bacteria using Open-Set Deep Learning-Driven Single-Cell Raman Spectroscopy”的研究论文。东莞理工学院为第一完成单位,袁玉峰博士为论文第一作者兼共同通讯作者,深圳大学彭晓副教授、屈军乐教授为论文共同通讯作者。

细胞在复杂的培养环境下具有显著的异质性,这使得单细胞分辨精度识别和判定细菌的生长状态,一直存在巨大的技术瓶颈。在多种细菌共生的复杂环境下,精准监测细菌的生理状态变化,有效排除其他细菌的干扰,对防控人畜共源性传染疾病具有重要的科学意义。在本文中,研究团队创新地构建了一种开放式深度学习驱动的单细胞拉曼光谱分析平台,通过融入阈值和邻近置信区间机制,克服传统深度学习封闭式预测分类的局限性,选取了13个不同生长代谢时间点,动态监控了短小芽孢杆菌(Bacillus pumilus)的芽孢化代谢进程,嵌入了3种芽孢杆菌的干扰。研究结果显示,本研究构建的开放式深度学习分析平台不仅能够实现对短小芽孢杆菌不同生长状态的精准预测识别(92.15±1.67%),而且可有效排除3种芽孢杆菌的干扰。对于未被纳入训练学习的细菌生长时间点,本论文构建的开放式深度学习分析平台借助邻近置信区间机制,为其赋予一个可信的生长时间判定。在多种细菌共生的实际场景下,本研究创建的开放式深度学习驱动的单细胞拉曼光谱分析平台,在鉴定并识别活菌的生长代谢状态方面具有巨大的应用潜力。
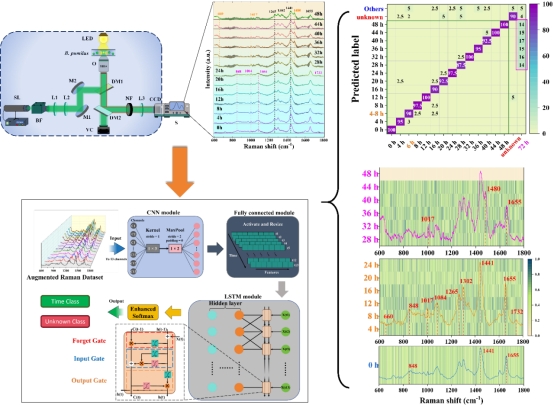
该研究成果得到国家自然科学基金面上项目(6207513),广东省自然科学基金粤莞联合基金地区培育项目(2023A1515140161)及东莞市社会发展科技重点项目(20231800936312)的资助。
论文链接:https://pubs.acs.org/doi/10.1021/acs.analchem.4c04817
(撰稿:袁玉峰;一审:邓敏君;二审:李艳霞;三审:张兆云 曾鹏举)